Images
L'equip internacional ho va aconseguir descobrint les regles que regeixen un tipus d'estructures de proteïnes que són essencials per a la interacció entre proteïnes i petites molècules
L'investigador de l'IRB Barcelona, Enrique Marcos, és el primer autor de l'estudi publicat avui a Science
Un equip internacional de científics liderats per la Universitat de Washington (UW) a Seattle ha desxifrat les regles clau que governen com les proteïnes formen estructures amb cavitats (semblants a butxaques) que són essencials per a moltes funcions clau de les proteïnes.
El descobriment permet que els investigadors dissenyin a mida proteïnes que poden imitar les accions de proteïnes naturals, així com dissenyar noves proteïnes, diferents de qualsevol altre que es trobi en la natura, hàbils per realitzar funcions totalment noves. Els resultats es publiquen en l'edició d’avui 13 de gener de la revista Science.
Actualment, els científics que miren de dissenyar una nova proteïna per actuar sobre una molècula particular acostumen a reutilitzar proteïnes naturals, però aquesta estratègia té diverses limitacions.
El primer autor d'aquest estudi, Enrique Marcos, que actualment treballa al laboratori de Modesto Orozco a l'Institut de Recerca Biomèdica (IRB Barcelona), explica que "aquesta nova estratègia ens permetrà dependre menys de les proteïnes naturals i dissenyar proteïnes amb potencialitat per desenvolupar noves proves de diagnòstic i tractaments, i propòsits biotecnològics, com catalitzar reaccions per aconseguir processos industrials més eficients".
David Baker, director de l'Institut de Disseny de Proteïnes de la UW, que va dirigir la investigació, apunta que "aquest enfocament permetrà afinar la mida i la forma d'aquestes cavitats o butxaques perquè les proteïnes dissenyades a mida es puguin unir i actuar sobre una molècula específica, un procés anomenat unió de lligand".
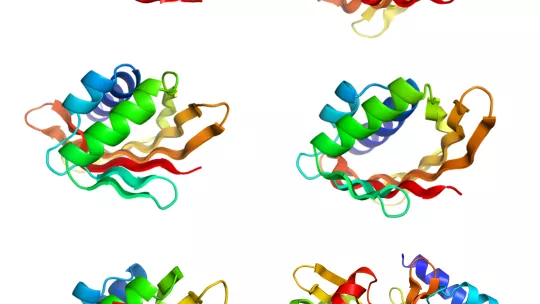
Les proteïnes estan formades per cadenes d'aminoàcids que es pleguen en una forma compacta que determina la seva funció. L'equip va estudiar les estructures que es formen quan cadenes dins de la mateixa proteïna s'alineen una al costat de l'altra per crear unes estructures laminars, anomenades fulles beta (fulles β). En moltes proteïnes naturals, aquestes fulles es dobleguen per formar cavitats que s'uneixen a les molècules diana implicades en molts processos cel·lulars.
Per desenvolupar la nova estratègia, els científics van identificar les propietats clau en la seqüència i orientació dels aminoàcids que determinen com les fulles β es pleguen i es corben.
Un cop identificades aquestes característiques, els investigadors mostren que és possible dissenyar per ordinador estructures de proteïnes i produir-les experimentalment amb alta precisió respecte del model computacional.
Aquestes proteïnes formen cavitats amb una varietat de formes i mides i a més demostren que són altament estables i toleren altes temperatures, el que és essencial per a l'enginyeria de noves funcions.
Article de referència:
Enrique Marcos, Benjamin Basanta, Tamuka M. Chidyausiku, Yuefeng Tang,Gustav Oberdorfer, Gaohua Liu, G.V.T. Swapna, Rongjin Guan, Daniel-Adriano Silva, Jiayi Dou, Jose Henrique Pereira, Rong Xiao, Banumathi Sankaran, Peter H. Zwart, Gaetano T. Montelione, David Baker
Principles for designing proteins with cavities formed by curved β-sheets
Science (2017). Doi: 10.1126/science.aah7389
IRB Barcelona
L’Institut de Recerca Biomèdica (IRB Barcelona) treballa per aconseguir una vida lliure de malalties. Desenvolupa una recerca multidisciplinària d’excel·lència per curar el càncer i altres malalties vinculades a l'envelliment. Treballa establint col·laboracions amb la indústria farmacèutica i els principals hospitals per fer arribar els resultats de la recerca a la societat a través de la transferència de tecnologia, i du a terme diferents iniciatives de divulgació científica per mantenir un diàleg obert amb la ciutadania. L’IRB Barcelona és un centre internacional que acull al voltant de 400 investigadors de més de 30 nacionalitats. Reconegut com a Centre d'Excel·lència Severo Ochoa des de 2011, és un centre CERCA i membre del Barcelona Institute of Science and Technology (BIST).