Images
Es tracta d’un software per analitzar i comprendre a través de mapes de fàcil interpretació el gran volum de dades epigenètiques i genètiques disponibles.
El treball és fruit de la complicitat entre bioestadístics, investigadors biocomputacionals i biòlegs moleculars de l’IRB Barcelona. Les capacitats de ChroGPS la demostren en un article a Nucleic Acids Resarch.
ChroGPS és un software per facilitar l’anàlisi i la comprensió de les dades epigenètiques i extreure’n informació intel·ligible, que es pot descarregar gratuïtament a Bioconductor, un repositori de referència de software biocomputacional. Els investigadors l'IRB Barcelona descriuen els usos del programa a la revista Nucleic Acids Research, on expliquen que ChroGPS és una resposta a un problema que s’arrossega des de fa una dècada.
En els darrers 15 anys, investigadors de tot el món han anat creant una gran quantitat d’informació sobre l’epigenoma: proteïnes, factors i marques epigenètiques que unides al DNA regulen l’expressió dels gens. Projectes multitudinaris com l’ENCODE (per humans i ratolins) o el modENCODE (per a altres sistemes model de laboratori, com la mosca Drosophila o el cuc C.Elegans) s’han dedicat a recollir aquestes dades per analitzar-les i interpretar-les en conjunt amb les dades genòmiques i extreure hipòtesis de funcions i relacions. Tot i aquests i d’altres esforços, hi ha una mancança d’eines que permetin extreure informació funcional i relacional de l’epigenoma i presentin els resultats d’una manera tan visual com ChroGPS.
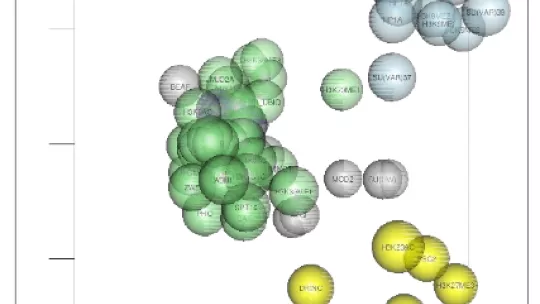
“Amb ChroGPS hem volgut integrar les dades epigenètiques amb les genètiques per treure’n tot el suc, que n’hi ha molt, i poder comprendre la informació que contenen. A dia d’avui els anàlisis són extremadament complexos i els resultats per interpretar les dades molt opacs”, diu Ferran Azorín, cap del laboratori d’Estructura i Funció de la Cromatina a l’Institut de Recerca Biomèdica (IRB Barcelona) i professor de recerca del CSIC, estudiós de la regulació epigenòmica. “Amb la nostra eina hem arribat a les mateixes conclusions que les presentades a Nature pels investigadors del modENCODE, però amb l’enorme diferència que en comptes de veure la informació amb centenars de gràfics i figures que va generar el modENCODE, ho hem aconseguit amb un únic mapa”, assenyala Azorín.
La iniciativa sorgeix del diàleg entre el grup d’Azorín, a través de l’estudiant de doctorat, Joan Font-Burgada, i el bioinformàtic Òscar Reina de l’equip de la Plataforma de Bioestadística i Bioinformàtica de l’IRB, liderada per David Rossell en aquell moment.
“ChroGPS es basa en l’ aplicació seqüencial de dos passos: primer, la generació de distàncies (o graus de similitud) entre elements epigenètics basant-nos en vàries mètriques possibles que hem desenvolupat, i després, en la representació d’aquestes distàncies en forma de mapes bi o tridimensionals per facilitar-ne la seva interpretació. Com ara els mapes visuals que es poden derivar d’aquelles taules de distàncies quilomètriques entre ciutats”, descriu Òscar Reina, un dels desenvolupadors.
“El més important per a nosaltres en aquesta primera etapa ha estat presentar informació biològica de forma senzilla, però alhora fiable des d’un punt de vista del tractament de les dades, per exemple corregint biaixos sistemàtics entre experiments que poden induir a conclusions errònies”, afegeix Rossell, avui a la Universitat de Warwick, al Regne Unit.
Ara que el programa ja està disponible com a codi obert per a tota la comunitat, els investigadors es plantegen nous reptes amb ChroGPS. Ferran Azorín té entre els objectius seguir un procés complex de transformació de cèl·lula normal en cancerosa a través dels canvis genètics i epigenètics que presenta. Per encarar aquest projecte amb ChroGPS, caldrà fer noves passes en metodologia estadística i matemàtica.
Article de referència:
chroGPS, a global chromatin positioning system for the functional analysis and visualization of the epigenome.
Joan Font-Burgada , Oscar Reina, David Rossell, and Fernando Azorín
Nucleic Acids Research (2013) doi:10.1093/nar/gkt1186
IRB Barcelona
L’Institut de Recerca Biomèdica (IRB Barcelona) treballa per aconseguir una vida lliure de malalties. Desenvolupa una recerca multidisciplinària d’excel·lència per curar el càncer i altres malalties vinculades a l'envelliment. Treballa establint col·laboracions amb la indústria farmacèutica i els principals hospitals per fer arribar els resultats de la recerca a la societat a través de la transferència de tecnologia, i du a terme diferents iniciatives de divulgació científica per mantenir un diàleg obert amb la ciutadania. L’IRB Barcelona és un centre internacional que acull al voltant de 400 investigadors de més de 30 nacionalitats. Reconegut com a Centre d'Excel·lència Severo Ochoa des de 2011, és un centre CERCA i membre del Barcelona Institute of Science and Technology (BIST).