Images
El avance logrado por investigadores del IRB Barcelona permite estudiar el rol de cada componente molecular en la estabilidad y conformación de los cristales de ADN.
Las nuevas técnicas de simulaciones moleculares reducirían el tiempo y el costo de obtención de cristales en laboratorio.
La cristalografía de rayos-X ha sido la técnica más usada desde el nacimiento de la biología estructural para determinar la estructura en tres dimensiones de las biomoléculas, los compuestos químicos que se encuentran en los organismos vivos. Esta técnica podría optimizarse si se conocieran las interacciones entre las biomoléculas con su entorno cristalino y las fuerzas moleculares que estabilizan los cristales.
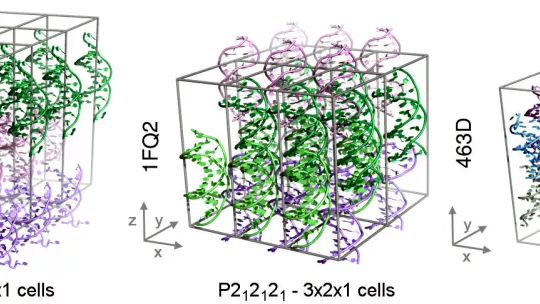
Un estudio publicado en la revista Chem, del grupo Cell, y elaborado por investigadores del Instituto de Investigación Biomédica (IRB Barcelona), ha logrado por primera vez simulaciones estables de cristales de ADN. Este hito ha permitido explicar la importancia de los aditivos químicos que se usan experimentalmente para lograr las condiciones de cristalización y obtener cristales estables en el laboratorio.
“El primer beneficiario de estudio es la comunidad de biofísicos y fisicoquímicos computacionales, quiénes cuentan ahora con una referencia y protocolos claros para obtener simulaciones estables de cristales de ADN”, afirma Pablo D. Dans, investigador postdoctoral del IRB Barcelona.
El estudio liderado por Modesto Orozco, jefe del laboratorio de Modelización Molecular y Bioinformática, presenta la descripción más detallada a nivel atómico de las propiedades de sistemas cristalinos con ADN presentada hasta la fecha.
“A largo plazo, la simulación de diversos cristales obtenidos en diferentes condiciones experimentales debería permitir anticipar y predecir el efecto de un aditivo químico dado, guiando a los cristalógrafos en sus experimentos y reduciendo considerablemente los costos y los tiempos de obtención de cristales”, subraya Modesto Orozco, catedrático de la Facultad de Química de la Universidad de Barcelona, cuyo laboratorio es uno de los referentes mundiales en computación y simulación de biomoléculas.
El estudio ha recibido fondos del Consejo Europeo de Investigación (ERC), a través del proyecto ERC Advanced Grant (SimDNA) otorgado a Modesto Orozco, y del Consorcio Europeo de Centros de Supercomputación a través de la beca PRACE 12th Call, otorgada a los tres autores del estudio.
Artículo de referencia:
Antonija Kuzmanic, Pablo D. Dans and Modesto Orozco.
An in-depth look at DNA crystals through the prism of molecular dynamics simulations
Chem (2019) DOI: 10.1016/j.chempr.2018.12.007
IRB Barcelona
El Instituto de Investigación Biomédica (IRB Barcelona) trabaja para conseguir una vida libre de enfermedades. Desarrolla una investigación multidisciplinar de excelencia para curar el cáncer y otras enfermedades vinculadas al envejecimiento. Establece colaboraciones con la industria farmacéutica y los principales hospitales para hacer llegar los resultados de la investigación a la sociedad, a través de la transferencia de tecnología, y realiza diferentes iniciativas de divulgación científica para mantener un diálogo abierto con la ciudadanía. El IRB Barcelona es un centro internacional que acoge alrededor de 400 científicos de más de 30 nacionalidades. Reconocido como Centro de Excelencia Severo Ochoa desde 2011, es un centro CERCA y miembro del Barcelona Institute of Science and Technology (BIST).