Images
Esta especie presenta abundantes duplicaciones génicas, lo que podría explicar su gran plasticidad y capacidad de adaptación a diferentes condiciones de cultivo.
El CSIC ha liderado este trabajo, que supone un importante avance en la construcción de herramientas genómicas y biotecnológicas para una producción acuícola más sostenible.
Los resultados del estudio son la base de nuevos programas de selección genética y programación ambiental para la mejorar la calidad de la progenie y la interacción con los microorganismos del ambiente en los que se cultiva la especie.
La dorada es una especie piscícola de gran importancia económica, ampliamente cultivada en todo el Mediterráneo, con una producción de más de 200.000 toneladas anuales. Su naturaleza hermafrodita, con una reversión macho-hembra a partir del segundo año de vida, junto con su capacidad de adaptación a cambios de salinidad, temperatura, disponibilidad de oxígeno y composición del alimento, ha sido una de las claves del éxito de su cultivo. Con el fin de conocer la base genética de esta gran plasticidad, investigadores de los Grupos de Nutrigenómica y de Patología de Peces del Instituto de Acuicultura Torre de la Sal del CSIC (IATS-CSIC) han liderado a lo largo de cuatro años un trabajo de secuenciación del genoma de esta especie, en colaboración con la empresa Biotechvana S.L. y el Centro de Regulación Genómica (CRG) de Barcelona.
El porqué de un gran número de genes y de duplicaciones génicas
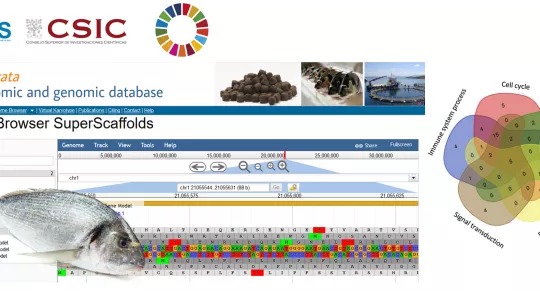
La estrategia de secuenciación masiva y de ensamblaje ha permitido obtener la versión más completa hasta la fecha de la secuencia del genoma de esta especie. “Hemos secuenciado y ensamblado más de 1.250 millones de pares de bases, de un total estimado de 1.600 millones” explica Jaume Pérez-Sánchez, Profesor de Investigación del CSIC y líder del proyecto. Se trata de un tamaño considerablemente mayor de lo encontrado en otras especies de peces de interés en acuicultura como la lubina y el rodaballo. Como resultado, se han identificado más de 55.000 genes que se expresan de forma activa, aunque lo más destacable es que más de la mitad de ellos, concretamente el 55%, presentan múltiples copias, “muchas de ellas generadas por elementos genéticos móviles”, según explica Carlos Llorens, responsable de Biotechvana.
“Gran parte de estas multiplicaciones no se corresponden con los sucesos evolutivos de duplicación ya conocidos en peces, sino que son propias de esta especie y por tanto recientes en términos evolutivos”, según comenta Toni Gabaldón, Investigador del CRG. Además, se ha comprobado que muchos de los genes duplicados están implicados en la respuesta a cambios en el medio, como las respuestas inmunitaria o sensorial, así como en la transposición genómica. Por tanto, es de esperar que esta multiplicación de la maquinaria molecular mejore la capacidad de domesticación y de adaptación de la especie en un contexto hostil o de cambio global “que requiere respuestas rápidas y apropiadas en sistemas de cultivo intensivo con una alta carga de patógenos”, según comenta Ariadna Sitjà-Bobadilla, Investigadora del Grupo de Patología del IATS.
Ejemplos de la gran plasticidad fenotípica de la dorada
La dorada es por tanto un modelo excelente para comprender los procesos que producen la expansión reciente del genoma en vertebrados superiores y las consecuencias que acaba teniendo ello sobre la plasticidad fenotípica de la especie. Como prueba de ello, engordes llevados a cabo en las instalaciones de cultivo del IATS en Castellón, demuestran que el metabolismo de un carnívoro como el de la dorada es suficientemente dúctil como para que sea posible producir doradas de 1 kg con tan sólo 1,2 kg de pienso, usando dietas basadas en ingredientes vegetales con un bajo contenido en harinas y aceites de pescado según las formulaciones propuestas en el proyecto europeo ARRAINA.
Asimismo, estudios llevados a cabo en colaboración con investigadores de la Universidad de las Palmas de Gran Canaria, dentro del Proyecto europeo PerformFish, han demostrado en un trabajo recientemente publicado en la revista Epigenetics (doi: 10.1080/15592294.2019.1699982) “que es posible programar nutricionalmente la progenie mediante cambios en la alimentación de los parentales que afectan a genes claves del metabolismo lipídico, como la delta-9-desaturasa”, según explica Jaume Pérez-Sánchez.
Otros ejemplos de la plasticidad fenotípica de la dorada se han evidenciado en el marco del Proyecto europeo de Infraestructuras en Acuicultura, AQUAEXCEL2020. En este caso, Josep Calduch-Giner, Investigador del grupo de Nutrigenómica del IATS, explica que “la exposición temprana a bajas concentraciones de oxígeno permite reprogramar metabólicamente a los animales para que meses después sean capaces de maximizar la producción de energía de forma aeróbica cuando sean retados con concentraciones bajas de oxígeno, por ejemplo, durante el periodo estival de rápido crecimiento”. No conocemos los mecanismos últimos, pero “posiblemente un papel clave lo jueguen los cambios observados en la composición de la microbiota intestinal”, según explica Carla Piazzon, Investigadora del Grupo de Patología del IATS.
Los investigadores han puesto a disposición pública y de la comunidad científica un visualizador del nuevo genoma de la dorada en su página web (www.nutrigroup-iats.org/seabreamdb). La investigación ha contado con financiación nacional (Proyecto Intramural del CSIC 1201530E025; BreamAquaINTECH, RTI2018-094128-B-I00) y europea (proyecto AQUAEXCEL2020), y ha sido publicada en la revista Frontiers in Marine Science.
Jaume Pérez-Sánchez, Fernando Naya-Català, Beatriz Soriano, M. Carla Piazzon, Ahmed Hafez, Toni Gabaldón, Carlos Llorens, Ariadna Sitjà-Bobadilla y Josep A. Calduch-Giner. Genome sequencing and transcriptome analysis reveal recent species-specific gene duplications in the plastic gilthead sea bream (Sparus aurata). Frontiers in Marine Science 6:760. DOI: https://doi.org/10.3389/fmars.2019.00760
IRB Barcelona
El Instituto de Investigación Biomédica (IRB Barcelona) trabaja para conseguir una vida libre de enfermedades. Desarrolla una investigación multidisciplinar de excelencia para curar el cáncer y otras enfermedades vinculadas al envejecimiento. Establece colaboraciones con la industria farmacéutica y los principales hospitales para hacer llegar los resultados de la investigación a la sociedad, a través de la transferencia de tecnología, y realiza diferentes iniciativas de divulgación científica para mantener un diálogo abierto con la ciudadanía. El IRB Barcelona es un centro internacional que acoge alrededor de 400 científicos de más de 30 nacionalidades. Reconocido como Centro de Excelencia Severo Ochoa desde 2011, es un centro CERCA y miembro del Barcelona Institute of Science and Technology (BIST).