Images
El equipo internacional lo logró descubriendo las reglas que rigen un tipo de estructuras de proteínas que son esenciales para la interacción entre proteínas y pequeñas moléculas
El investigador del IRB Barcelona, Enrique Marcos, es el primer autor del estudio publicado hoy en Science
Un equipo internacional de científicos liderados por la Universidad de Washington (UW) en Seattle ha descifrado las reglas clave que gobiernan cómo las proteínas forman estructuras con cavidades (parecidos a bolsillos) que son esenciales para muchas funciones clave de proteínas.
El descubrimiento permite que los investigadores diseñen a medida proteínas que pueden imitar las acciones de proteínas naturales, así como diseñar proteínas desde cero, diferentes a cualquiera que se encuentre en la naturaleza, capaces de realizar funciones totalmente nuevas. Los resultados se publican hoy en la edición del 13 de enero de la revista Science.
Actualmente, los científicos que tratan de diseñar una nueva proteína para actuar sobre una molécula particular suelen reutilizar proteínas naturales, pero esta estrategia tiene varias limitaciones. El primer autor de este estudio, Enrique Marcos, que actualmente trabaja en el laboratorio de Modesto Orozco del Instituto de Investigación Biomédica (IRB Barcelona), explica que "esta nueva estrategia nos permitirá depender menos de las proteínas naturales y diseñar proteínas con potencialidad para desarrollar nuevas pruebas de diagnóstico y tratamientos, o para propósitos biotecnológicos, como catalizar reacciones para conseguir procesos industriales más eficientes".
David Baker, director del Instituto de Diseño de Proteínas de la UW, qque dirigió la investigación, apunta que "este enfoque permitirá afinar el tamaño y la forma de estas cavidades o bolsillos para que las proteínas diseñadas a medida se pueden unir y actuar sobre una molécula específica, un proceso llamado unión de ligando”.
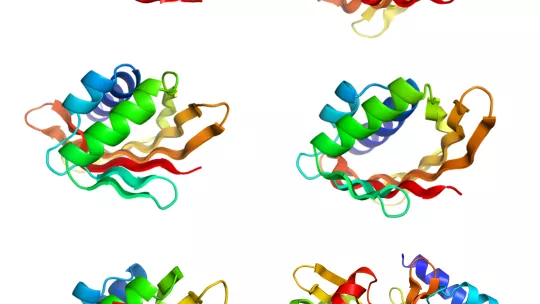
Las proteínas están formadas de cadenas de aminoácidos que se pliegan en una forma compacta que determina su función. El equipo estudió las estructuras que se forman cuando cadenas dentro de la misma proteina se alinean una junto a otra para crear unas estructuras laminares, llamadas hojas beta (hojas β). En muchas proteínas naturales, estas hojas se doblan para formar cavidades que se unen a las moléculas diana implicadas en muchos procesos celulares.
Para desarrollar la nueva estrategia, los científicos identificaron las propiedades clave en la secuencia y orientación de los aminoácidos que determinan cómo las hojas β se pliegan y se curvan. Una vez identificadas estas características, los investigadores muestran que es posible diseñar computacionalmente estructuras de proteínas y producirlas experimentalmente con alta precisión respecto del modelo computacional. Dichas proteínas forman cavidades con una variedad de formas y tamaños y además demuestran que son altamente estables y toleran altas temperaturas, lo que es esencial para la ingeniería de nuevas funciones.
Artículo de referencia:
Enrique Marcos, Benjamin Basanta, Tamuka M. Chidyausiku, Yuefeng Tang,Gustav Oberdorfer, Gaohua Liu, G.V.T. Swapna, Rongjin Guan, Daniel-Adriano Silva, Jiayi Dou, Jose Henrique Pereira, Rong Xiao, Banumathi Sankaran, Peter H. Zwart, Gaetano T. Montelione, David Baker
Principles for designing proteins with cavities formed by curved β-sheets
Science (2017). Doi: 10.1126/science.aah7389
IRB Barcelona
El Instituto de Investigación Biomédica (IRB Barcelona) trabaja para conseguir una vida libre de enfermedades. Desarrolla una investigación multidisciplinar de excelencia para curar el cáncer y otras enfermedades vinculadas al envejecimiento. Establece colaboraciones con la industria farmacéutica y los principales hospitales para hacer llegar los resultados de la investigación a la sociedad, a través de la transferencia de tecnología, y realiza diferentes iniciativas de divulgación científica para mantener un diálogo abierto con la ciudadanía. El IRB Barcelona es un centro internacional que acoge alrededor de 400 científicos de más de 30 nacionalidades. Reconocido como Centro de Excelencia Severo Ochoa desde 2011, es un centro CERCA y miembro del Barcelona Institute of Science and Technology (BIST).