Images
Investigadors de laboratori de Bioinformàtica Estructural i Biologia de Xarxes de l'IRB Barcelona desenvolupen un sistema per predir la resposta d'un tumor a diferents teràpies.
S’anomena “Targeted Cancer Therapy for You” (TCT4U), i amb ell s'han identificat un conjunt de biomarcadors complexos que estan disponibles per a la comunitat mèdica-científica.
El treball ha estat publicat a la revista Genome Medicine.
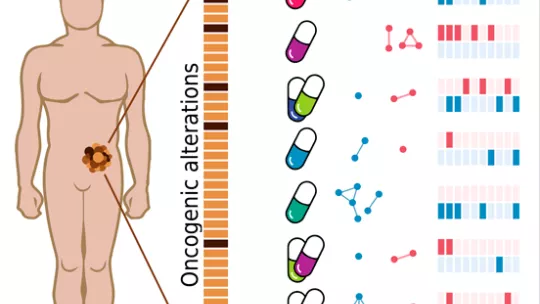
Els gens conductors del càncer són aquells que presenten mutacions essencials per al desenvolupament i l'expansió del tumor. Investigadors del laboratori de Bioinformàtica Estructural i Biologia de Xarxes (SBNB) de l'IRB Barcelona, liderats per l'investigador ICREA Patrick Aloy, han desenvolupat un sistema informàtic que prediu la resposta d'un tumor a diferents tractaments del càncer. Aquest sistema es basa en la identificació de marcadors complexos de resposta derivats dels patrons de coocurrència entre gens conductors del càncer que presentin mutacions. El sistema s'ha posat a prova experimentalment i amb dades de pacients de càncer de mama, i ha pogut predir la resposta a les diferents teràpies amb un 66% d'encert.
Els gens conductors del càncer, pel seu paper crucial en el desenvolupament del tumor, són un important tema d'estudi en les últimes dècades. Conèixer els gens conductors del càncer, que estan afectats en un tumor concret, pot contribuir a identificar l'enfocament terapèutic més apropiat per a un determinat pacient, en un apropament al que es coneix com a “medicina de precisió”. Per primera vegada, els investigadors de laboratori SBNB, proposen la coocurrència (o la seva absència) d'alteracions en dos o més gens conductors del càncer, com a factor clau per a predir la resposta a un determinat tractament.
"La suma de dos o més gens conductors del càncer afectats per mutacions genera una xarxa complexa de biomarcadors, altera el perfil molecular del tumor i repercuteix en la seva resposta als tractaments", diu Aloy. "Amb aquest treball, veiem que estudiar els gens conductors del càncer en el seu conjunt, analitzant les diferents combinacions, pot suposar un gran avenç envers la medicina de precisió", afegeix.
Des de la bioinformàtica a l'anàlisi experimental i clínica
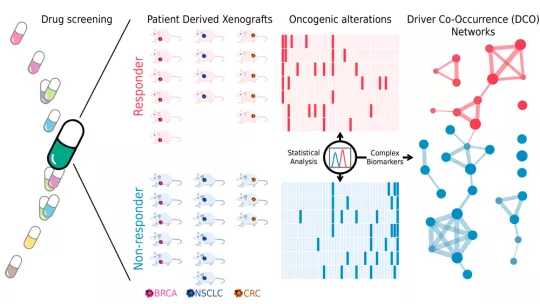
Tot i la disponibilitat de dades genomes del càncer, no existeix tanta informació sobre el resultat de les intervencions terapèutiques en pacients. Els investigadors van partir d'una base de dades pública que recull informació sobre l'efecte de múltiples tractaments sobre el creixement de tumors humans que han estat implantats en un model de ratolí. Partint d'aquestes dades, van seleccionar 53 tractaments (o combinacions de tractaments) i van comparar el perfil molecular dels tumors que responien a cada tractament amb els que no ho feien.
"Quan ja havíem desenvolupat el nostre model computacional, el validem experimentalment en tumors humans implantats en ratolí", diu Lídia Mateo, investigadora postdoctoral de laboratori SBNB i primera autora de l'estudi. "Vam ser capaços de predir el resultat que tindria la teràpia en 12 dels 14 casos d'estudi, molt per sobre del poder de predicció de la resposta a fàrmacs dels biomarcadors aprovats", afegeix. Els investigadors també van validar l'algoritme amb dades de resposta a tractaments de pacients amb càncer de mama.
El treball, publicat a Genome Medicine, s'ha dut a terme en col·laboració amb l'Institut d'Oncologia Vall d'Hebron (VHIO) i amb el Memorial Sloan Kettering Cancer Center (MSKCC), que va permetre aplicar el sistema predictiu a l'anàlisi de resultats d'assaigs clínics.
Aquest treball ha estat finançat per l'European Research Council, el Ministeri de Ciència i Innovació I la Generalitat de Catalunya. Lídia Mateo compta amb una Beca FPI.
Article de referència:
Lidia Mateo, Miquel Duran-Frigola, Albert Gris-Oliver, Marta Palafox, Maurizio Scaltriti, Pedram Razavi, Sarat Chandarlapaty, Joaquin Arribas, Meritxell Bellet, Violeta Serra & Patrick Aloy
Personalized cancer therapy prioritization based on driver alteration co-occurrence patterns
Genome Medicine (2020) DOI: 10.1186/s13073-020-00774-x
IRB Barcelona
L’Institut de Recerca Biomèdica (IRB Barcelona) treballa per aconseguir una vida lliure de malalties. Desenvolupa una recerca multidisciplinària d’excel·lència per curar el càncer i altres malalties vinculades a l'envelliment. Treballa establint col·laboracions amb la indústria farmacèutica i els principals hospitals per fer arribar els resultats de la recerca a la societat a través de la transferència de tecnologia, i du a terme diferents iniciatives de divulgació científica per mantenir un diàleg obert amb la ciutadania. L’IRB Barcelona és un centre internacional que acull al voltant de 400 investigadors de més de 30 nacionalitats. Reconegut com a Centre d'Excel·lència Severo Ochoa des de 2011, és un centre CERCA i membre del Barcelona Institute of Science and Technology (BIST).